Luigi Ricciardi 1 , Rosa Mazzeo 2,*© ၊ Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1 © နှင့် Concetta Lotti 2,*
- 1 Department of Soil, Plant and Food Sciences, Plant Genetics and Breeding Unit University of Bari, Via Amendola 165/A, 70125 Bari, Italy; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (လက်မောင်း); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 စိုက်ပျိုးရေး၊ အစားအသောက်နှင့် သဘာဝပတ်ဝန်းကျင်သိပ္ပံဌာန၊ University of Foggia၊ Via Napoli 25၊ 71122 Foggia၊ အီတလီ
- 3 ဇီဝသိပ္ပံ၊ ဇီဝနည်းပညာနှင့် ဇီဝဆေးဝါးများဌာန၊ Bari တက္ကသိုလ်၊ Via Orabona 4၊ 70125 Bari၊ အီတလီ၊ guglielmo.rainaldi@uniba.it
- 4 စွမ်းအင်နည်းပညာဌာန၊ ဇီဝစွမ်းအင်၊ ဇီဝသန့်စင်ရေးနှင့် စိမ်းလန်းသောဓာတုဗေဒဌာနခွဲ၊ ENEA Trisaia သုတေသနဌာန၊ SS 106 Ionica၊ ကီလိုမီတာ 419+500၊ 75026 Rotondella (MT)၊ အီတလီ၊ paolo.iovieno@enea.it
* စာပေးစာယူ: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
စိတ္တဇ:
ကြက်သွန်နီ ( Allium cepa L.) သည် ကမ္ဘာတစ်ဝှမ်းတွင် ဒုတိယအရေးကြီးဆုံး ဟင်းသီးဟင်းရွက်သီးနှံဖြစ်ပြီး ၎င်း၏ကျန်းမာရေးအကျိုးကျေးဇူးများအတွက် ကျယ်ကျယ်ပြန့်ပြန့် တန်ဖိုးထားလေးစားပါသည်။ ၎င်း၏ ထင်ရှားသော စီးပွားရေးဆိုင်ရာ အရေးပါမှုနှင့် ၎င်း၏တန်ဖိုးကို လုပ်ဆောင်နိုင်သော အစားအစာအဖြစ် ကြက်သွန်နီသည် ၎င်း၏မျိုးရိုးဗီဇကွဲပြားမှုနှင့်စပ်လျဉ်း၍ စုံစမ်းစစ်ဆေးမှု အားနည်းခဲ့သည်။ ဤနေရာတွင်၊ Bari (အီတလီနိုင်ငံတောင်ပိုင်း၊ Apulia၊ Apulia) ရှိ မြို့ငယ်လေးတွင် ရာစုနှစ်တစ်ခုကြာ စိုက်ပျိုးခဲ့သည့် သမိုင်းကြောင်းရှိသော မြေယာဖြစ်သော “Acquaviva Red ကြက်သွန်နီ” (ARO) တွင် မျိုးရိုးဗီဇကွဲလွဲမှုကို စစ်တမ်းကောက်ယူခဲ့သည်။ ARO လူဦးရေ 11 ဦးနှင့် ဘုံစီးပွားဖြစ် အမျိုးအစားသုံးမျိုးပါဝင်သော ပိုးမွှားအစုအဝေးတစ်ခုတွင် မျိုးရိုးဗီဇကွဲပြားမှုကို စူးစမ်းရန်အတွက် မိုက်ခရိုဂြိုဟ်တု အမှတ်အသား ၁၁ ခုကို အသုံးပြုခဲ့သည်။ ARO သည် မကြာခဏ လွဲမှားလေ့ရှိသော Tropea နှင့် Montoro ကုန်းမြေမှ ပြတ်ပြတ်သားသား ကွဲပြားသော ကောင်းစွာသတ်မှတ်ထားသော မျိုးရိုးဗီဇရေကန်ကို ကိုယ်စားပြုသည့် ပါရာမက်ထရစ်နှင့် မဟုတ်သော ပါရာမက်ထရစ်နည်းများဖြင့် မျိုးဗီဇဖွဲ့စည်းပုံကို ခွဲခြမ်းစိတ်ဖြာထားသည်။ လတ်ဆတ်သောစားသုံးမှုအတွက်အသုံးပြုလေ့ရှိသော မီးသီးများ၏ဖော်ပြချက်ပေးရန်အတွက်၊ ပျော်ဝင်နိုင်သောအစိုင်အခဲပါဝင်မှုနှင့် အမှုန်အမွှားများကို အကဲဖြတ်ပြီး အထက်ဖော်ပြပါမြေနေရာနှစ်ခုနှင့်စပ်လျဉ်း၍ ARO တွင် ပိုမိုချိုမြိန်မှုကိုပြသသည်။ ယေဘုယျအားဖြင့်၊ လက်ရှိလေ့လာမှုသည် စီးပွားဖြစ်လိမ်လည်မှုများကို ကန့်သတ်ရန်နှင့် အသေးစားလုပ်ကွက်ငယ်များ၏ ၀င်ငွေကို မြှင့်တင်ပေးနိုင်သည့် အရည်အသွေးတံဆိပ်များမှတစ်ဆင့် မြှင့်တင်နိုင်စေမည့် ARO ၏ အနာဂတ်တန်ဖိုးသတ်မှတ်မှုအတွက် အသုံးဝင်သည်။
နိဒါန္း
The Allium genus includes about 750 species [1], among which onion (Allium cepa L., 2n = 2x =16) is one of the most widespread. A. cepa has a biennial cycle and outcrossing reproductive behavior. Nowadays, onion global production (97.9 Mt) makes it the second most important vegetable crop after tomato [2]. Since olden times, onion bulbs have been used both as food and in folk medicinal applications. Indeed, ancient Egyptians already reported several therapeutic formulas based on the use of garlic and onions in a medical papyrus of the 1550 BC, the Codex Ebers [3].
စွယ်စုံရကျန်းမာသော ဤဟင်းသီးဟင်းရွက်ကို အစိမ်းလိုက်၊ လတ်ဆတ်သော သို့မဟုတ် ပြုပြင်ထားသော ထုတ်ကုန်အဖြစ် စားသုံးပြီး ဟင်းပေါင်းများစွာ၏ အရသာကို မြှင့်တင်ရန်အတွက် အသုံးပြုပါသည်။ မကြာသေးမီက လေ့လာမှုများစွာအရ ကြက်သွန်နီစားသုံးခြင်းသည် နှလုံးသွေးကြောဆိုင်ရာရောဂါများ [4,5]၊ အဝလွန်ခြင်း [6]၊ ဆီးချိုရောဂါ [7] နှင့် ကင်ဆာပုံစံအမျိုးမျိုး [8-10] ဖြစ်နိုင်ခြေကို လျှော့ချနိုင်သည်ဟု ဆိုကြသည်။ ကြက်သွန်နီ၏ ကျန်းမာရေးဆိုင်ရာ ဂုဏ်သတ္တိများကို အာဟာရဓာတ် အမျိုးအစား နှစ်မျိုးဖြစ်သော flavonoids နှင့် alk(en)yl cysteine sulphoxides (ACSOs) ၏ မြင့်မားသော အဆင့်ကြောင့် မကြာခဏ ရည်ညွှန်းပါသည်။ ပထမတန်းစားတွင် flavonols နှင့် anthocyanins ပါဝင်သည်။ Quercetin သည် ၎င်း၏ ပြင်းထန်သော ဓာတ်တိုးဆန့်ကျင်မှုနှင့် ရောင်ရမ်းမှုကို ဆန့်ကျင်သည့် ဂုဏ်သတ္တိများကြောင့် လူသိများသော အဓိက ရှာဖွေတွေ့ရှိနိုင်သော ဖလေဗွန်နောဖြစ်ပြီး၊ ဖရီးရယ်ဒီကယ်များကို ဖယ်ရှားခြင်းနှင့် အကူးအပြောင်း သတ္တုအိုင်းယွန်းများ ပေါင်းစပ်ခြင်းတွင် လူသိများသည်။ [11]; Anthocyanins သည် ကြက်သွန်မျိုးကွဲအချို့တွင် အနီရောင်/ခရမ်းရောင်ကို ပေးစွမ်းသည်။ ACSO များအတွက် အပေါများဆုံးမှာ isoalliin [(+)-trans-S-1-propenyl-L-cysteine sulfoxide]၊ [12]ကြက်သွန်နီ၏ ညှော်နံ့နှင့် အရသာအတွက် သွယ်ဝိုက်တာဝန်ယူသည့် ဆဲလ်များတွင် သိုလှောင်ထားသော မတည်ငြိမ်သောနှင့် ပရိုတင်းဓာတ်မဟုတ်သော ဆာလဖာအမိုင်နိုအက်ဆစ်၊ [13]. တစ်သျှူးများ ပြတ်တောက်သွားသောအခါတွင်၊ isoalliin အား ကိုက်ဖြတ်ခြင်းနှင့် မနှစ်မြို့ဖွယ် အနံ့အသက် (pungency) ဖြစ်ပေါ်စေသည့် မငြိမ်မသက်သော ဒြပ်ပေါင်းများ (pyruvate၊ ammonia၊ thiosulphonates နှင့် propanethial S-oxide) ကို ထုတ်လုပ်ရန် အယ်လီနိုင်နင်း အင်ဇိုင်းဖြင့် ထွင်းထုထားသည်။ [14]. ကြက်သွန်နီအဆိပ်သင့်ခြင်းကို hydrolysis မှထုတ်ပေးသော pyruvic acid ၏ လတ်ဆတ်သောအလေးချိန်တစ်ဂရမ်လျှင် ပမာဏအဖြစ် တိုင်းတာလေ့ရှိသည်။ [15၊၁].
မြေထဲပင်လယ်ဒေသရှိ နိုင်ငံများတွင် အလယ်တန်းမတူကွဲပြားမှုစင်တာများထဲမှ တစ်ခုအဖြစ် အဆိုပြုထားသည်။ A. cepa [17၊၁]၊ ကြက်သွန်မီးသီးများသည် ပုံသဏ္ဍာန်၊ အရွယ်အစား၊ အရောင်၊ ခြောက်သွေ့မှုနှင့် အမှုန်အမွှားကွဲပြားမှုကို ပြသသည် [19စာ-၁]. ထို့အပြင်၊ ဆာလဖာအခြေခံမြေသြဇာ၊ စိုက်ပျိုးရေးဆိုင်ရာအလေ့အထများ၊ မြေအမျိုးအစား၊ ရာသီဥတုအခြေအနေနှင့် မျိုးရိုးဗီဇဆိုင်ရာ မျိုးရိုးဗီဇဆိုင်ရာ ဇီဝကမ္မဖြစ်စဉ်များနှင့် အာဟာရတန်ဖိုးများကို ပေးဆောင်ခြင်းဖြင့် မီးသီးအရည်အသွေးကို လွှမ်းမိုးနိုင်သည်။ [23စာ-၁]. အီတလီတွင် ကြက်သွန်နီ ပိုးမွှားများ ကျယ်ပြန့်စွာ ရရှိနိုင်သော်လည်း၊ ကြက်သွန်နီမျိုးကွဲ အနည်းငယ်ကိုသာ သိပ္ပံနည်းကျ လေ့လာမှုများ ပြုလုပ်လေ့ရှိပြီး မှန်ကန်သော လက္ခဏာရပ်များ ရှိကြောင်း၊ [28၊၁].
Thoroughly genetic and phenotypic characterization of agro-biodiversity is crucial to assure appropriate conservation of plant genetic resources and promote the use of specific genotypes in the value chain [30စာ-၁]. မြေပုံဆွဲခြင်းအတွက် ရိုးရှင်းသော sequence repeat (SSR) အမှတ်အသားများကို မကြာခဏ ရွေးချယ်ထားသည်။ [33စာ-၁]DNA လက်ဗွေနှိပ်ခြင်းနှင့် မျိုးရိုးခွဲခြားခြင်း [36စာ-၁]၊ နှင့် မြေနေရာများအတွင်းနှင့် မျိုးရိုးဗီဇကွဲပြားမှု၏ ယုံကြည်စိတ်ချရသော ခန့်မှန်းချက် [39စာ-၁], since they are locus specific, multi-allelic, codominantly inherited, highly reproducible, and suitable for automated genotyping.
ယခုလေ့လာမှုတွင်၊ Bari ပြည်နယ်၊ Acquaviva delle Fonti မြို့၏သေးငယ်သောဧရိယာတွင် အော်ဂဲနစ်စိုက်ပျိုးရေးနည်းလမ်းများအတိုင်း စိုက်ပျိုးထားသည့် "Acquaviva ကြက်သွန်နီ" (ARO) သည် Apulian ရိုးရာမြေကွင်းကို အာရုံစိုက်ခဲ့ပါသည်။ (Apulia၊ အီတလီတောင်ပိုင်း)။ ဤကွင်း၏မီးသီးများသည် ကြီးမားပြီး ပြားသွားကာ အနီရောင်ရှိပြီး ဒေသထွက် ဟင်းချက်နည်းများတွင် အများစုအသုံးပြုကြသည်။ ARO သည် "Slow Food Presidium" အရည်အသွေးအမှတ်အသားကို ရရှိခဲ့သော်လည်း၊ ၎င်းကို ကန့်သတ်ရန်အတွက် ကန့်သတ်ရန် အထောက်အကူဖြစ်စေနိုင်သောကြောင့် ၎င်း၏ထုတ်လုပ်မှုကို ကန့်သတ်ရန် အထောက်အကူဖြစ်စေနိုင်သောကြောင့် ၎င်း၏ထုတ်လုပ်မှုကို ကန့်သတ်ရန် အထောက်အကူဖြစ်စေနိုင်သောကြောင့် ၎င်း၏ထုတ်လုပ်မှုကို ကန့်သတ်ရန် အထောက်အကူဖြစ်စေနိုင်သည် စီးပွားဖြစ် လိမ်လည်မှုများနှင့် အသေးစား လုပ်ငန်းရှင်များ၏ ဝင်ငွေ တိုးတက်စေခြင်း။ ဤနေရာတွင်၊ SSR မော်လီကျူးအမှတ်အသားများကို ARO လူဦးရေများကြားတွင် မျိုးရိုးဗီဇကွဲလွဲမှုကို အကဲဖြတ်ရန်နှင့် အခြားအီတလီတောင်ပိုင်းကြက်သွန်နီကုန်းမြေဧရိယာနှစ်ခုမှ ဤနယ်မြေကို ခွဲခြားရန် အစွမ်းထက်သောကိရိယာများအဖြစ် အသုံးပြုခဲ့သည်။ ထို့အပြင်၊ စျေးကွက်ဝယ်လိုအားနှင့်ဆက်စပ်၍ ARO အရသာအကဲဖြတ်ရန်အတွက် ကျွန်ုပ်တို့သည် အမှုန်အမွှားနှင့် ပျော်ဝင်နိုင်သော အစိုင်အခဲအကြောင်းအရာများကို ခန့်မှန်းတွက်ချက်ပါသည်။
ရလဒ်များ
Establishment of Acquaviva Red Onion Germplasm Collection and Morphological Characterization
BiodiverSO Apulia Region ပရောဂျက်၏ မူဘောင်အရ လယ်သမားများမှ လှူဒါန်းသော ARO Landrace ၏ လူဦးရေ 13 မျိုး၏ မျိုးစေ့များကို ARO ပိုးမွှားများ စုစည်းမှု ထူထောင်ရန်အတွက် အသုံးပြုခဲ့သည်။
မီးသီး၊ အရေပြားနှင့် အသားနှင့် ဆက်စပ်သော ဇီဝဗေဒဆိုင်ရာ ဖော်ပြချက်များအား ARO ပိုးမွှားများနှင့် ကြက်သွန်နီကုန်းမြေ ၃ ခုတွင် စုဆောင်းခဲ့သည်၊ "Tropea red onion" (TRO) landrace မှ နှစ်ခုနှင့် "Montoro copper onion" (MCO) landrace (ပုံ 1). ARO မီးသီးအားလုံးသည် ပြားချပ်ချပ်ဖြစ်ပြီး အနီရောင် ပြင်ပအရေပြားနှင့် အသားများဖြင့် ကွဲပြားသော အနီရောင်အရိပ်များ ရှိသည်။ ဆန့်ကျင်ဘက်အားဖြင့်၊ TRO မီးသီးများ၏ အသားသည် အနီရောင်ဖြစ်ပြီး MCO မီးသီးများ၏ အသားသည် အရောင်ခြယ်မှု ညံ့ဖျင်းသည် (ဇယား S1)။ ဇီဝဓာတုခွဲခြမ်းစိတ်ဖြာခြင်းသည် အစိုင်အခဲပျော်ဝင်နိုင်သော အကြောင်းအရာနှင့် အမှုန်အမွှားများကို အကဲဖြတ်ရန် ခွင့်ပြုထားသည်။ ဇယားမှာဖော်ပြထားတဲ့အတိုင်း 1, ARO လူဦးရေများတွင် မီးသီးများ၏ အစိုင်အခဲပျော်ဝင်နိုင်သော အကြောင်းအရာများ၏ ပျမ်းမျှတန်ဖိုးများမှာ 7.60 ဖြစ်ပြီး 6.00 (ARO12) မှ 9.50° Brix (ARO11 နှင့် ARO13) တို့ဖြစ်သည်။ ဤတန်ဖိုးသည် TRO နှင့် MCO Landraces (4.25 နှင့် 6.00° Brix အသီးသီး) အတွက် ခန့်မှန်းထားသည်ထက် ပိုများသည်။

စားပွဲတင် 1 ။ “Acquaviva Red Onion” (ARO)၊ “Tropea Red Onion” (TRO) နှင့် “Montoro Copper ကြက်သွန်နီ” (MCO) လူဦးရေ * တွင် အကဲဖြတ်ထားသော အခဲပျော်ဝင်နိုင်သော အကြောင်းအရာနှင့် Pungency တန်ဖိုးများ။
| ကုတ် | ပျော်ဝင်နိုင်သော အစိုင်အခဲ အကြောင်းအရာ (Brix) | Pungency (pmolg-1 FW) | ||
| ဆိုလို | CV y (%) | ဆိုလို | CV y (%) | |
| ARO1 | 6.25 D * | 5.65 | 5.84 ab* | 23.78 |
| ARO2 | 7.25 DC က | 4.87 | 6.51 မှ | 22.98 |
| ARO3 | 7.50 BCD | 9.42 | သာသနာနှစ် ၆ | 22.88 |
| ARO4 | 7.50 BCD | 0.00 | 6.97 မှ | 3.74 |
| ARO ၅ | 7.50 BCD | 0.00 | 6.80 မှ | 9.68 |
| ARO6 | 6.25: D | 5.65 | သာသနာနှစ် ၆ | 39.18 |
| ARO7 | 7.25 DC က | 4.87 | သာသနာနှစ် ၆ | 15.44 |
| ARO8 | 9.00 AB | 0.00 | 7.04 မှ | 3.49 |
| ARO9 | 8.25 ABC | 4.28 | 6.84 မှ | 0.15 |
| ARO10 | 7.00 DC က | 0.00 | သာသနာနှစ် ၆ | 6.57 |
| ARO11 | 9.50 တစ်ဦးက | 7.44 | သာသနာနှစ် ၆ | 16.43 |
| ARO12 | 6.00: D | 0.00 | သာသနာနှစ် ၆ | 9.70 |
| ARO13 | 9.50 တစ်ဦးက | 7.44 | 6.63 မှ | 24.93 |
| MCO | 6.00: D | 0.00 | သာသနာနှစ် ၆ | 2.66 |
| TRO1 | 4.25 E ကို | 8.31 | 2.80 ခ | 2.10 |
| TRO2 | 4.25 E ကို | 8.31 | သာသနာနှစ် ၆ | 4.79 |
* Means with the same letters in uppercase or lowercase are not statistically different at 0.01P or 0.05P, respectively (SNK’s Test). y ကွဲလွဲမှု၏ကိန်းဂဏန်း။
pyruvic acid ပါဝင်မှုဖြင့် အကဲဖြတ်သော ARO pungency ၏ ပျမ်းမျှတန်ဖိုးမှာ 6.00 ဖြစ်ပြီး 4.51 pmol g မှ-1 FW (ARO6) မှ 7.04 (ARO8)။ ဤတန်ဖိုးသည် TRO နှင့် MCO မြေနေရာများတွင် ခန့်မှန်းထားသည်ထက် (3.54 pmol g-1 FW နှင့် 4.18 pmol g-1 FW, respectively).
SSR Polymorphism and Genetic Relationships among Accessions
လက်ရှိလေ့လာမှုတွင်၊ စမ်းသပ်ထားသော SSR primer ပေါင်းစပ်မှု ၃၇ ခုတွင် ၁၁ ခုသည် single-locus polymorphisms များကို ပေးဆောင်သည်၊ ဆိုလိုသည်မှာ၊ တစ်ခုချင်းစီတွင် ချဲ့ထွင်မှုထုတ်ကုန်နှစ်ခုအများစုကို အထွက်နှုန်းဖြစ်စေသည်။ ယေဘုယျအားဖြင့် 11 (ACM37 နှင့် ACM 55) မှ 320 (ACM2) နှင့် ပျမ်းမျှတန်ဖိုး 147 alleles (ဇယား 2). လူတစ်ဦးချင်းစီတွင်၊ အယ်လီလီများ (Na) အရေအတွက်သည် 1.94 (ACM147 နှင့် ACM504) မှ 5.38 (ACM132) အထိရှိသော်လည်း ထိရောက်သော alleles (Ne) အရေအတွက်မှာ 1.41 (ACM152) မှ 2.82 (ACM449) အထိရှိသည်။ ကွဲလွဲမှုများ between Na and Ne values were due to the presence of alleles with low frequency in the populations and the predominance of only a few alleles. The highest observed heterozygosity (Ho) value was highlighted for ACM138 and ACM449 (0.62), whereas the lowest one was associated with ACM152 (0.25). Expected heterozygosity (He), which corresponds to the theoretical expectation in a panmictic population, ranged from 0.37 (ACM504) to 0.61 (ACM132, ACM138, and ACM449). The Wright’s fixation index (Fis), displayed values close to zero (average 0.05) for all the markers, indicating similar values between observed and expected heterozygosity levels, as expected for an outcrossing species. The efficiency of individual SSR marker in genetic fingerprinting was estimated by the polymorphic information content (PIC) index, with a mean value of 0.48 and ranged from 0.33 (ACM504) to 0.67 (ACM132). Another efficiency index, the Shannon’s Information Index (I) displayed a mean value of 0.84, and assumed values ranged from 0.45 (ACM152) to 1.20 (ACM132).
စားပွဲတင် 2 ။ ARO၊ TRO နှင့် MCO လူဦးရေများတွင် မျိုးရိုးဗီဇကွဲပြားမှုကို ခန့်မှန်းရန် အသုံးပြုသည့် SSR အမှတ်အသား 11 ခု၏ Polymorphism အင်္ဂါရပ်များ။ Alleles (Na) စုစုပေါင်းအရေအတွက်၊ Band Size Range နှင့် Polymorphic Information Content (PIC) Index သည် ဤလေ့လာမှုတွင် Genotyped တစ်ဦးချင်းစီ စုစုပေါင်း 320 ကို ရည်ညွှန်းပါသည်။ Alleles အရေအတွက် (Na)၊ Effective Alleles အရေအတွက် (Ne)၊ Observed Heterozygosity (Ho)၊ Expected Heterozygosity (He)၊ Fixation Index (Fis) နှင့် Shannon ၏ အချက်အလက်အညွှန်းကိန်း (I) သည် လူဦးရေ 16 ဦးမှ တွက်ချက်ထားသော ပျမ်းမျှတန်ဖိုးများကို ရည်ညွှန်းပြီး၊ တစ်ခုချင်းစီတွင် လူ 20 ဖြင့် ဖွဲ့စည်းထားသည်။
| နေရာ။ | Total Na | အရွယ်အစား အတိုင်းအတာ (bp) | PIC | ဆိုလို | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| ဆိုလို | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
လူဦးရေများထဲတွင် ARO3၊ ARO6၊ ARO8၊ ARO10၊ TRO1 နှင့် MCO သည် မျိုးရိုးဗီဇကွဲလွဲမှုအဆင့် (Ho > 0.5) ကိုပြသခဲ့ပြီး ARO7 (Ho = 0.27) (နောက်ဆက်တွဲဇယား S2) တွင် အနိမ့်ဆုံးကွဲပြားမှုကို တွေ့ရှိရပါသည်။ ယေဘုယျအားဖြင့် F တွင်ပြသထားသောဆက်စပ်ပစ္စည်းများအားလုံးis သုညနှင့်နီးစပ်သောတန်ဖိုးများ (Fis ပျမ်းမျှတန်ဖိုး = 0.054)၊ ကျပန်းမိတ်လိုက်သည့်အခြေအနေများအောက်တွင် မျှော်လင့်ထားသည့်အတိုင်း။
Molecular Variance နှင့် Genetic Structure ကို လေ့လာခြင်း။
Hierarchical partitioning of genetic variation among and within populations was computed by AMOVA. The results highlighted a considerable fraction of genetic variation within populations (87%). Variation among populations, 13%, was highly significant (P < 0.001) (ဇယား 3). 0.002 (ARO2/ARO10) မှ 0.468 (ARO7/TRO2) မှ Wright's Fst fixation အညွှန်းကိန်း၏ တူညီသော တူညီသော Fpt ပါရာမီတာ၏ Pairwise တန်ဖိုးများသည် သိသာထင်ရှားသည် (P < 0.05)၊ အတွဲလိုက် နှိုင်းယှဉ်မှု ကိုးခုမှလွဲ၍ (နောက်ဆက်တွဲဇယား S3)။
စားပွဲတင် 3 ။ လူဦးရေ 320 ဦးမှ Genotypes 16 ၏ မော်လီကျူးကွဲလွဲမှုကို လေ့လာခြင်း။ allium cepa L.
| အရင်းအမြစ် | df | ရင်ပြင်၏ပေါင်းလဒ် | ကွဲပြားမှု ခန့်မှန်းချက် | ကွဲလွဲမှု (%) | Fpt | P |
| Among populations | 15 | 458.63 | 1.16 | 13% | ||
| လူဦးရေအတွင်း | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| စုစုပေါင်း | 319 | 2731.62 | 8.66 |
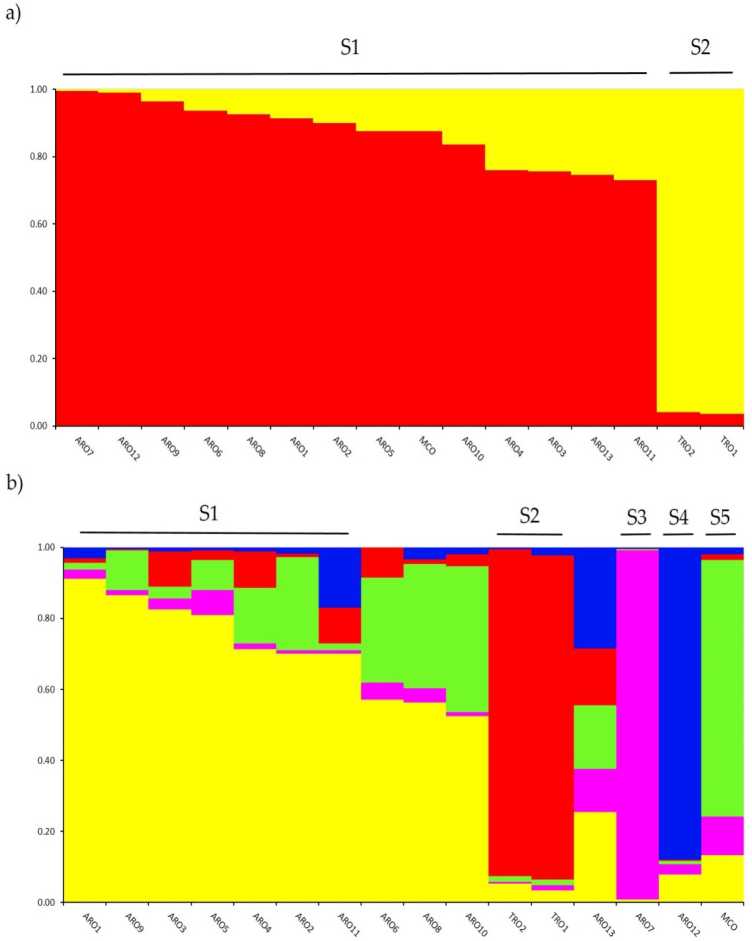
မျိုးရိုးဗီဇဖွဲ့စည်းပုံကို စုံစမ်းစစ်ဆေးခြင်း။ A. cepa collection genotyped in this study was performed by means of the admixture model-based clustering analysis implemented in the software STRUCTURE. The Evanno AK method suggested subdivision in two clusters (K = 2) as the most informative for our Datasets,နှင့်အတူe လာမယ့် pe အမြင့်ဆုံးak at K = 5 (sopplementaiv Rgure S1)။ တစ်ဦးက အမဲချိတ် = 2, aကောင်ရေopulations wမြည်းigned onနှင့်f နှစ်ခုပြွတ် နှင့် a rnernbertoip coefficient (q) > 0.7။ ၎hown in ဂဏန်း 2a, the first cluster (named S1) included MCO and all ARO populations, whereas the S2 cluster grouped the two TRO populations. At K = 5, providing a deeper description of the dataset (Figure 2b) ပါဝင်ခွင့်များ၏ 75% ကို အစုအဖွဲ့ငါးခုမှ တစ်ခုသို့ တာဝန်ပေးအပ်ခဲ့သည်။ ARO (S1) နှင့် TRO (S2) အကြား ပိုင်းခြားမှုကို အတည်ပြုထားသော်လည်း အချို့သော ARO လူဦးရေများ (q < 0.7) ကို ပေါင်းစပ်ထားသည် သို့မဟုတ် အစုအသစ် S3 နှင့် S4 (ARO7 နှင့် ARO12 အသီးသီး) တွင် သီးခြားစီခွဲထားသည်။ စိတ်ဝင်စားစရာမှာ MCO သည် စီးပွားဖြစ်အမျိုးအစားသည် Apulian ကြက်သွန်နီနှင့် သီးခြားခွဲထားသော ကွဲပြားသောအစုအဝေး (S5) ကို ဖြစ်ပေါ်စေခဲ့သည်။
လူဦးရေများအကြား မျိုးရိုးဗီဇဆိုင်ရာ ဆက်ဆံရေး
SSR polymorphism သည် မျိုးရိုးဗီဇကွဲပြားမှု၏ dendrogram ကိုဆွဲရန်ခွင့်ပြုထားပြီး phylogenetic ခွဲခြမ်းစိတ်ဖြာမှု၏ရလဒ်များကိုပုံတွင်ပြသထားသည်။ 3a. Here, the germplasm collection was splitted in five groups strongly supported by bootstrap values. The ARO7 and ARO12 populations were immediately separated from the remaining populations and formed two distinct clusters. The third cluster included the two commercial populations of TRO, meanwhile the fourth node divided MCO from eleven ARO populations. Genetic relationship occurring among populations was further investigated by means of principal coordinate analysis (PCoA) (Figure 3b) ယခင်က မီးမောင်းထိုးပြထားသည့်အတိုင်း၊ ARO လူဦးရေများကို PCoA ကွက်လပ်တွင် သီးခြားနေရာများတွင် တွေ့ရသည့် ARO12 နှင့် ARO7 တို့မှလွဲ၍ ARO လူဦးရေများကို တင်းကျပ်စွာ အုပ်စုဖွဲ့ထားသည်။ TRO နှစ်ခုနှင့် MCO လူဦးရေများသည် မြေကွက်၏ ညာဘက်အောက်ပိုင်း၌ ပြန့်ကျဲနေသည်။
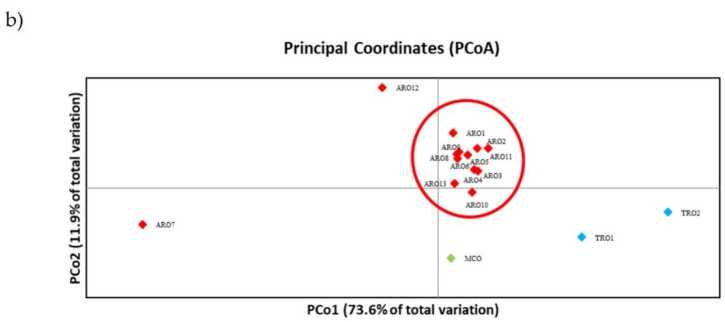
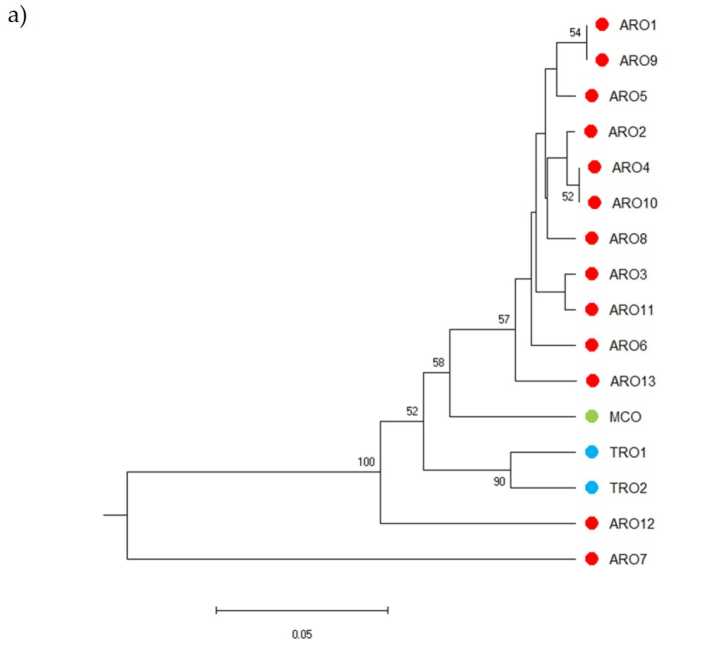
ပုံ 3 ။ Genetic diversity among 16 A. cepa ၎င်းတို့၏ SSR ပရိုဖိုင်အပေါ် အခြေခံ၍ ဤလေ့လာမှုတွင် လက္ခဏာရပ်များ။ (aမျိုးရိုးဗီဇအကွာအဝေး၏ UPGMA denrogram။ Bootstrap ပံ့ပိုးမှုတန်ဖိုးများ >50 သည် သက်ဆိုင်ရာ node များအထက်တွင် ဖော်ပြထားပါသည်။ (b) principal component analysis (PCoA). The cluster circled in red fully matched with the group generated by phylogenetic analysis and constituted by 11 ARO accessions.
ဆွေးနွေးမှု
အီတလီတောင်ပိုင်းတွင် ရိုးရာဇီဝမျိုးစုံမျိုးကွဲများ အများအပြားစိုက်ပျိုးသော ပမာဏအတွင်းတွင် ကြက်သွန်နီများသည် မျိုးရိုးလိုက်စားမှုအန္တရာယ်နှင့် ခေတ်မီမျိုးစိတ်များ အစားထိုးခြင်းအန္တရာယ်မှ ထိန်းသိမ်းထားရန် လိုအပ်သော အထူးထုတ်ကုန်များကို ကိုယ်စားပြုပါသည်။ ဒေသဆိုင်ရာ အမွေအနှစ်များနှင့် ခိုင်ခိုင်မာမာဆက်စပ်နေသည့် Apulia ဒေသ၏ မျိုးရိုးဗီဇအရင်းအမြစ်များကို စုဆောင်းခြင်း၊ အသွင်လက္ခဏာပြခြင်း၊ မြှင့်တင်ခြင်းနှင့် ကာကွယ်စောင့်ရှောက်ခြင်းအတွက် ရည်ရွယ်သော BiodiverSO ၏ မူဘောင်တွင်၊ ကျွန်ုပ်တို့သည် ARO Landrace ၏ လူဦးရေ 13 ဦး၏ မျိုးစေ့စုဆောင်းခြင်းကို တည်ထောင်ခဲ့ပါသည်။ DNA polymorphisms နှင့် biochemical parameters နှစ်ခု၊ ပျော်ဝင်နိုင်သော အစိုင်အခဲနှင့် pyruvic acid ပါဝင်မှုများ၊ အရသာ လက္ခဏာများနှင့် လတ်ဆတ်သော မချက်ပြုတ်ရသေးသော ထုတ်ကုန်များကို လက်ခံရရှိမှုအတွက် အရေးပါမှုတို့နှင့် သက်ဆိုင်သည့် ARO ကွဲလွဲမှု၏ ပထမဆုံး အကဲဖြတ်ချက်ကို အစီရင်ခံပါသည်။ ထို့အပြင်၊ ARO Landrace ရှိ ဒေတာကို အခြားအရောင်ခြယ်ထားသော ကြက်သွန်နီ စိုက်ခင်းနှစ်ခုတွင် စုဆောင်းထားသည့် အချက်အလက်များနှင့် မကြာခဏ လွဲမှားလေ့ရှိသည်။
ဇီဝဓာတုဗေဒ ခွဲခြမ်းစိတ်ဖြာချက်များအရ ကြက်သွန်မွှေးလုပ်ငန်း လမ်းညွှန်ချက်များအရ မြင့်မားသော ပျော်ဝင်နိုင်သော အစိုင်အခဲပါဝင်မှုနှင့် လတ်ဆတ်သော အညှောင့်ဆက်စပ်မှုရှိသော ARO လူဦးရေ ၁၃ ဦး၏ အချိုဓာတ်ကို မီးမောင်းထိုးပြခဲ့သည်။ [31]. ARO bulbs were sweeter than those of the TRO and MCO landraces, and displayed a slightly higher pungency. However, sweetness in onions is due to a balance between sugar content and pungency, therefore this characterization could be useful to support the selection of genotypes of value, usually carried out by farmers only based on the morphology.
SSR markers were confirmed to be a useful tool to discriminate genotypes, albeit collected within a narrow growing area such as the town of Acquaviva delle Fonti. The selected markers displayed higher number of alleles than the markers previously reported by [43] နှင့် [44]ဒါပေမယ့် ဖော်ပြထားတဲ့ အမှတ်အသားတွေထက် နိမ့်ပါတယ်။ [45]. Moreover, 50% of our set of markers showed PIC index values greater than 0.5, proving to be suitable to discriminate the populations in the collection, as suggested by [46]. လူဦးရေအတွင်း မတူကွဲပြားမှုများကို အကဲဖြတ်ခြင်းသည် ဟိုနှင့် သူကြားတွင် အလားတူတန်ဖိုးများကို ဖော်ပြခဲ့ပြီး Fi ကို နည်းပါးစေသည်။s တန်ဖိုးများ ဤသည်မှာ ဖြတ်ကျော်ခြင်းသဘောသဘာဝနှင့် ကိုက်ညီပါသည်။ A. cepa၊ ပေါက်ဖွားလာသော စိတ်ကျရောဂါကို ပြင်းထန်စွာ ခံစားနေရသည်။ [47]. The overall Fis ဤလေ့လာမှုတွင် ထည့်သွင်းစဉ်းစားထားသော ကြက်သွန်နီလူဦးရေအတွက် တွက်ချက်ထားသော တန်ဖိုး (၀.၀၅၄) သည် ယခင်ဖော်ပြခဲ့သည့် ပမာဏထက် နည်းပါးနေပါသည်။ [45] (0.22) သည် တွေ့ရှိသည့်အရာနှင့် နီးပါးတူညီသည်။ [31] (0.08) နှင့် [48] (0.00) who assessed genetic diversity in onion landraces from northwest Spain and Niger, respectively. Noteworthy levels of heterozygosity in ARO populations reinforce the notion that Apulia represents a diversity center for many horticultural species [32, 42, 49စာ-၁].
AMOVA သည် ဤလေ့လာမှုတွင် စုစည်းထားသော မျိုးရိုးဗီဇဆိုင်ရာ မော်လီကျူးကွဲလွဲမှုအများစုသည် လူဦးရေများအတွင်းတွင်ရှိကြောင်း AMOVA မှ မီးမောင်းထိုးပြခဲ့သည်။ သို့သော် လူဦးရေများအကြား သိသာထင်ရှားသော မျိုးရိုးဗီဇ ကွဲပြားမှု (FPT တန်ဖိုးများ) မျိုးရိုးဗီဇ ကွဲပြားခြင်း၏ ပေါ်ပေါက်မှုကို ထင်ရှားစေသည်။ တကယ်တော့၊ ကျွန်ုပ်တို့၏ရလဒ်များသည် ARO လူဦးရေအများစုတွင် မျိုးရိုးဗီဇတူညီမှုရှိနေခြင်းကို ကောင်းစွာသတ်မှတ်ထားသောအစုအဝေးတစ်ခုအဖြစ် ညွှန်ပြသော်လည်း ARO7 နှင့် ARO12 လူဦးရေများသည် ရှင်းရှင်းလင်းလင်းကွဲပြားသောမျိုးဗီဇဆိုင်ရာပရိုဖိုင်ကိုပြသခဲ့သည်။ ဤရလဒ်သည် လယ်သမားနှစ်ဦးမှ စုဆောင်းခဲ့သည့် မျိုးစေ့များ၏ မူလဇာစ်မြစ် မတူညီခြင်းကြောင့် ဖြစ်နိုင်သည်။ ထို့အပြင် ရရှိသော ရလဒ်များအပေါ် အခြေခံ၍ ARO Landrace ကို TRO နှင့် MCO landraces များမှ မျိုးရိုးဗီဇအဆင့်တွင် ရှင်းရှင်းလင်းလင်း ကွဲပြားသည်ဟု ယူဆနိုင်ပါသည်။ မကြာသေးမီက လေ့လာမှုတစ်ခုတွင်၊ [29] “Acquaviva” “Tropea” နှင့် “Montoro” အပါအဝင် အီတလီ ကြက်သွန်နီ အမျိုးအနွယ် အများအပြား၏ မျိုးရိုးဗီဇ ကွဲပြားမှုကို အကဲဖြတ်ခဲ့သည်။ စာရေးဆရာများသည် ပိုမိုကျယ်ပြန့်သော ကြက်သွန်နီစုဆောင်းမှု၏ မျိုးရိုးဗီဇကွဲပြားမှုကို အကဲဖြတ်ရန် SNP အမှတ်အသားများကို အသုံးပြုခဲ့သော်လည်း မျိုးရိုးလိုက်ခြင်းသည် "Tropea" နှင့် "Montoro" ကြက်သွန်နီများမှ "Acquaviva" ကို ခွဲခြား၍မရပါ။ ဖြစ်နိုင်သည်မှာ၊ ဤကွာဟချက်မှာ တွေ့ရှိရသည့် ပျမ်းမျှ PIC တန်ဖိုး (0.292) ကြောင့်ဖြစ်သည်၊ ခွဲခြမ်းစိတ်ဖြာမှုအောက်တွင် loci ၏ အနည်းငယ်မျှသာသော ယေဘုယျအချက်အလက်များကို ညွှန်ပြနေသောကြောင့်ဖြစ်သည်။ [29]. Furthermore, in order to investigate the presence of sub-structure in their Italian cluster, it would have been better to analyze the Italian genotypes separately from the rest of the collection. Probably it would have allowed to visualize pattern of genetic diversity linked to geographic stratification or traits under empiric selection.
In conclusion, the present study represents a comprehensive report on an onion landrace associated with local cultural heritage and of economic importance for the farmers. Our results highlight that, with a few exceptions, ARO is characterized by a well-defined gene pool, which deserves to be preserved from the risk of genetic erosion. Therefore, the establishment of a representative collection of this valuable source of genetic diversity has been crucial. Finally, the genetic and phenotypic characterization of ARO might be useful to obtain quality marks from the European Union.
ကုန်ကြမ်းနှင့်နည်းစနစ်များ
Germplasm Collection, Plant Material, and DNA Extraction
A set of 13 populations of the ARO landrace were acquired within the framework of an Apulia Region project (BiodiverSO: https://www.biodiversitapuglia.it/)အီတလီနိုင်ငံ၊ Bari ပြည်နယ်ရှိ Apulian မြို့ငယ်လေးဖြစ်သော “Acquaviva delle Fonti” တွင် လုပ်ဆောင်ခဲ့သော မစ်ရှင်များ ဆက်တိုက်အားဖြင့်။ ချိတ်ဆက်မှုတစ်ခုစီ၏ စုစည်းဆိုက်များကို Geographic Information System (GIS) မှတဆင့် မြေပုံဆွဲပြီး ဇယားတွင် အစီရင်ခံပါသည်။ 4. ထို့အပြင်၊ TRO Landrace မှလူဦးရေ 41 ဦးနှင့် MCO Landrace မှလူဦးရေတစ်ဉီးတို့ကို ပစ္စုပ္ပန်လေ့လာမှုတွင် ထည့်သွင်းပြီး အကိုးအကားအဖြစ် အသုံးပြုခဲ့သည်။ ဝတ်မှုန်ကူးမကူးမီ ၀တ်မှုန်ကူးခြင်းကို ရှောင်ရှားရန် လှောင်အိမ်အောက်တွင် ၀တ်မှုန်ကူးမရအောင် ကာကွယ်သည့် လှောင်အိမ်အောက်တွင် အပင်ထွက်ပစ္စည်းအားလုံးကို Bari တက္ကသိုလ်မှ P Martucci (1°22.08'16″ N, 54°25.95'XNUMX″ E)၊ လူဦးရေနှင့် လူဦးရေအတွင်း ၀တ်မှုန်ကူးခြင်းကို မှုတ်ထုတ်ခြင်းဖြင့် အာမခံပါသည်။ (Lucilia caesar). လူဦးရေ 16 ဦးသည် မီးသီးအရွယ်အစားနှင့် ပုံသဏ္ဍာန်နှင့် အသားအရောင်နှင့် အသားအရောင် (Table S1) တို့နှင့်ဆက်စပ်သော စရိုက်လက္ခဏာများအတွက် လက္ခဏာရပ်များဖြစ်သည်။ ထို့အပြင်၊ အစိုင်အခဲပျော်ဝင်နိုင်သော အကြောင်းအရာ စစ်ဆေးမှုအား လက်ကိုင် refractometer ဖြင့် တိုင်းတာပြီး 2,4-dinitrophenyl hydrazine (0.125% ကို ကြက်သွန်နီဖျော်ရည်နမူနာများတွင် တိုင်းတာခဲ့သည်။ v/v in 2N of HCl) and evaluating absorbance at 420 nm, as reported by [31]. Duncan ၏ multiple-range test နှင့် SNK test တို့သည် သိသာထင်ရှားသော ကွဲပြားမှုများ ရှိနေခြင်းကို ဆုံးဖြတ်ရန် လုပ်ဆောင်ခဲ့ကြသည်။
စားပွဲတင် 4 ။ ဤလေ့လာမှုတွင် စုဆောင်းပြီး မျိုးရိုးလိုက်သော လူဦးရေစာရင်း။ လူဦးရေတစ်ခုစီအတွက်၊ သက်သေခံကုဒ်၊ ဒေသအမည်၊ GPS ညှိနှိုင်းဆောင်ရွက်မှုနှင့် မျိုးစေ့များကို ထိန်းသိမ်းစောင့်ရှောက်သည့် ဗီဇဘဏ်တို့ကို အစီရင်ခံထားသည်။
| ကုဒ် | အမည် | ဂျီပီအက်စ် Coordinates | ဗီဇဘဏ် y |
| ARO1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO9 | Cipolla rossa di Acquaviva | 40°54''51.372" N 16°49''3.504" E | Di.SSPA |
| ARO10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO11 | Cipolla rossa di Acquaviva | 40°52''49.8" N 16°49''48.575" E | Di.SSPA |
| ARO12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA၊ မြေဆီလွှာ၊ အပင်နှင့် အစားအသောက်သိပ္ပံဌာန၊ Bari တက္ကသိုလ်။ |
Leaf material of 20 genotypes per population were sampled and stored at -80 °C until use. For polysaccharide-rich species, as A. cepa၊ polysaccharide ဖယ်ရှားခြင်း ပထမအဆင့်များသည် အရည်အသွေးကောင်း DNA ရရှိရန် မရှိမဖြစ်လိုအပ်သောကြောင့် STE ကြားခံတွင် ကနဦးဆေးကြောခြင်း (0.25 M sucrose, 0.03 M Tris, 0.05 M EDTA) တို့ကို ဖော်ပြထားသည့်အတိုင်း လုပ်ဆောင်ခဲ့ပါသည်။ [52]. စုစုပေါင်း DNA ကို CTAB နည်းလမ်းဖြင့် ထုတ်ယူခဲ့သည်။ [53] and finally it was checked for quality and concentration by Nano Drop 2000 UV-vis spectrophotometer (ThermoScientific, Waltham, MA, USA) and 0.8% agarose gel electrophoresis.
SSR ခွဲခြမ်းစိတ်ဖြာခြင်း။
16 EST-SSR primer ပေါင်းစပ်မှုဖြင့် ထုတ်လုပ်သည်။ [54] မျိုးရိုးဗီဇကွဲပြားမှုဆိုင်ရာ လေ့လာမှုများတွင် ယခင်စမ်းသပ်မှုများ ပြုလုပ်ခဲ့သည်။ [43] နှင့် [44] 21 မျိုးဗီဇ SSR [45စာ-၁] ၎င်းတို့၏ သင့်လျော်မှုကို အကဲဖြတ်ရန် (နောက်ဆက်တွဲဇယား S4) ကို စိစစ်ခဲ့သည်။ M13 အမြီးကို forward SSR primer တစ်ခုစီတွင် ထည့်ထားသည့် စီးပွားရေး fluorescent tagging နည်းလမ်းကို အသုံးပြု၍ Genotyping လုပ်ဆောင်ခဲ့သည် [56]. PCR ရောစပ်ထားသော 20 gL တုံ့ပြန်မှုတွင်- စုစုပေါင်း DNA ၏ 50 ng ၊ dNTP ရောနှောမှု 0.2 mM ၊ PCR တုံ့ပြန်မှုကြားခံ 1X ၊ DreamTaq DNA polymerase ၏ 0.8 U ( Thermo Scientific ၊ Waltham ၊ MA ၊ USA ) ၊ ပြောင်းပြန် primer 0.16 gM ပါဝင်သည် ၊ M0.032 အစီအစဥ် (13′-TGTAAAACGACGGCCAGT-5′) နှင့် FAM သို့မဟုတ် NED ချောင်းဆိုးဆေးဖြင့် တံဆိပ်တပ်ထားသော universal M3 primer ၏ 0.08 gM နှင့် FAM သို့မဟုတ် NED ချောင်းဆိုးဆေး (Sigma-Aldrich, St. Louis, MO, USA)။ PCR တုံ့ပြန်မှုများကို SimpliAmp (Applied Biosystems, CA, USA) သာမိုစက်ဘီးများတွင် အောက်ပါအခြေအနေများဖြင့် လုပ်ဆောင်ခဲ့သည်- 13 မိနစ်အတွက် 94°C၊ 5s အတွက် 40°C တွင် 94 cycles၊ 30°C၊ 58 စက္ကန့်နှင့် 45 ဒီဂရီစင်တီဂရိတ်တွင် 72 စက္ကန့်နှင့် 45 ဒီဂရီစင်တီဂရိတ်တွင် 72 မိနစ်ကြာအောင် နောက်ဆုံး ရှည်သည်။ ACM5 နှင့် ACM446 အတွက်၊ 449°C မှ 60°C တွင် 55 cycles ကျော် ၊ 10°C တွင် 30 cycles နှင့် touchdown PCR ကို 55°C တွင် 5 mins တွင် နောက်ဆုံး သက်တမ်းတိုးခြင်းဖြင့် သက်ရောက်ပါသည်။ PCR ထုတ်ကုန်များကို 72 ရေတွင်းပန်းကန်ပြားတစ်ခုထဲသို့ တင်ဆောင်ပြီး Hi-Di Formamide 96 gL (Life Technologies, Carlsbad, CA, USA) နှင့် 14 gL GeneScan 0.5 ROX Size Standard (Life Technologies, Carlsbad, CA, USA) တို့နှင့် ရောနှောထားသည်။ Amplicons သည် ABI PRISM 500 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, USA) သွေးကြောမျှင်များကို စီစစ်ခြင်းစက်ဖြင့် ဖြေရှင်းပေးခဲ့ပြီး၊ အယ်လီလီများကို တွဲဖက်လွှမ်းမိုးထားကာ GeneMapper ဆော့ဖ်ဝဲလ်ဗားရှင်း 3100 ကို အသုံးပြု၍ တာဝန်ပေးအပ်ခြင်းခံရသော Amplicons ကို ဖြေရှင်းပေးသည်။
GenAlEx 6.5 ဆော့ဖ်ဝဲများ [57] and Cervus 3.0.7 [58] alleles အရေအတွက် (Na)၊ ထိရောက်သော alleles အရေအတွက် (Ne)၊ သတိပြုမိသော heterozygosity (Ho)၊ မျှော်မှန်းထားသော heterozygosity (He)၊ polymorphic information content (PIC)၊ Shannon ၏ အချက်အလက်ညွှန်းကိန်း (I) နှင့် fixation အညွှန်းကိန်း (Fis ) SSR နေရာတစ်ခုစီအတွက်။
မျိုးရိုးဗီဇကွဲပြားမှု အကဲဖြတ်ခြင်း။
Hierarchical partitioning of genetic variation among and within the onion populations was evaluated by GenAlEx 6.5 [57] 999 bootstrapping ဖြင့် မော်လီကျူးကွဲလွဲမှု (AMOVA) ၏ ခွဲခြမ်းစိတ်ဖြာမှုမှတဆင့် အဓိပ္ပာယ်ကို စမ်းသပ်ရန်။ ထို့အပြင်၊ GenAlEx 6.5 ဆော့ဖ်ဝဲလ်ကို SSR loci အားလုံးတွင် ပျမ်းမျှ Ho၊ He နှင့် Fis တို့ကို တွက်ချက်ခြင်းဖြင့် လူဦးရေတစ်ခုစီအတွင်း ကွဲပြားမှုကို ခန့်မှန်းရန် အသုံးပြုခဲ့သည်။
STRUCTURE v.2.3.4 ဆော့ဖ်ဝဲလ်တွင် အသုံးပြုထားသည့် Bayesian မော်ဒယ်အခြေပြု အစုလိုက်အပြုံလိုက် အယ်လဂိုရီသမ်မှ လူဦးရေဖွဲ့စည်းပုံကို ကောက်ချက်ချခဲ့သည် [59]. ဒေတာအတွဲကို 1 မှ 10 အထိ ၊ 100,000 မှ 100,000 အထိ ၊ K တန်ဖိုးတစ်ခုစီတိုင်းတွင် အမှီအခိုကင်းသော ပြေးနှုန်း ဆယ်ခုကို သတ်မှတ်ပေးခြင်းဖြင့် ဒေတာအစုံကို လုပ်ဆောင်ခဲ့သည်။ ပြေးပွဲတစ်ခုစီအတွက် ရလဒ်များ၏ ညီညွတ်မှုကို စိစစ်ရန် ရည်ရွယ်၍ ကနဦး လောင်ကျွမ်းမှုကာလ XNUMX နှင့် Markov Chain Monte Carlo (MCMC) XNUMX တို့ကို ရောစပ်မှုပုံစံနှင့် လူဦးရေများအကြား လွတ်လပ်သော allele ကြိမ်နှုန်းများအောက်တွင် ပြုလုပ်ခဲ့သည်။ ဖြစ်နိုင်ခြေအရှိဆုံး K တန်ဖိုးကို ဖော်ပြထားသည့် AK နည်းလမ်းကို အကောင်အထည်ဖော်ရန် ဆုံးဖြတ်ခဲ့ခြင်းဖြစ်သည်။ [60], in the web-based program STRUCTURE HARVESTER [61]. ၎င်း၏အသင်းဝင်ဖော်ကိန်း (q-value) 0.7 ထက် မြင့်မားသောအခါတွင် တစ်ဦးချင်းလူဦးရေကို သီးသန့်အစုအဝေးတစ်ခုသို့ တာဝန်ပေးအပ်ခဲ့သည်
Nei ၏မျိုးရိုးဗီဇအကွာအဝေးမက်ထရစ် (နောက်ဆက်တွဲဇယား S5) မှဖော်ပြသောဆက်စပ်မှုများကြားတွင်မျိုးရိုးဗီဇဆိုင်ရာဆက်နွယ်မှုပုံစံများကိုမြင်ယောင်နိုင်ရန်အဓိကသြဒိနိတ်ခွဲခြမ်းစိတ်ဖြာမှုကိုလုပ်ဆောင်ခဲ့သည်။ allele ကြိမ်နှုန်းများအပေါ်အခြေခံ၍ POPTREEW ဆော့ဖ်ဝဲရှိ ဂဏန်းသင်္ချာပျမ်းမျှ (UPGMA) အစုအဝေးခွဲခြမ်းစိတ်ဖြာမှုဖြင့် အလေးမထားသောအတွဲအုပ်စုနည်းလမ်းကို အကောင်အထည်ဖော်ရန်အတွက် မျိုးရိုးဗီဇအကွာအဝေး၏ dendrogram တစ်ခုကို တည်ဆောက်ထားသည်။ [62]. ဒေတာအတွဲ၏ 100 ပြန်လည်နမူနာသတ်မှတ်ခြင်းတွင် အထက်အောက် အစုလိုက်ပြုလုပ်ခြင်းတွင် ယုံကြည်မှုကို အကဲဖြတ်ရန် Bootstrapping ကို အသုံးပြုထားသည်။ နောက်ဆုံးအနေနဲ့ MEGA X ဆော့ဝဲ [63] သစ်ပင်ပုံဆွဲဆော့ဖ်ဝဲအဖြစ် အသုံးပြုခဲ့သည်။
ဖြည့်စွက်ပစ္စည်းများ- အောက်ပါမှာအွန်လိုင်းရရှိနိုင်ပါသည် http://www.mdpi.com/2223-7747/9/2/260/s1. ဇယား S1- ARO၊ MCO နှင့် TRO မီးသီးများ၏ ဇီဝရုပ်လက္ခဏာများ။ ဇယား S2- ARO landraces နှင့် TRO နှင့် MCO landraces အတွက် တွက်ချက်ထားသော Heterozygosity နှင့် fixation indices။ ဇယား S3- Fpt ပါရာမီတာ၏ တန်ဖိုးများကို Pairwise တန်ဖိုးများ။ ဇယား S4- လေ့လာမှုတွင် အသုံးပြုသည့် SSR များစာရင်း။ ဇယား S5။ Nei မျိုးရိုးဗီဇအကွာအဝေး၏လူဦးရေ matrix တွဲလျက်။ ပုံ S1- Evanno ၏ Delta K ဖြင့် ပြောင်းလဲနေသော K တန်ဖိုးများ၏ လိုင်းဇယား။
စာရေးသူထောက်ပံ့: C.L. and L.R. conceived the study and designed the experiment; C.L. and P.I. performed molecular marker analysis; A.R.M. and V.Z. performed the field trials; R.M., S.P., G.R., and C.L. were involved in data analysis; R.M. and C.L. wrote the manuscript. All authors have read and agreed to the published version of the manuscript.
ရန်ပုံငွေရှာခြင်း: This work was funded by the Regional Apulian project “Biodiversity of Apulian vegetable species”—Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10—Sottomisura 10.2; grant CUP H92C15000270002, Italy.
ကျေးဇူးတင်လွှာ: Acknowledgements are due to “Azienda Agricola Iannone Anna” and “Associazione produttori della vera cipolla rossa di Acquaviva” for providing plant materials used in the experiment.
အကျိုးစီးပွား၏ပဋိပက္ခ: အဆိုပါစာရေးဆရာအကျိုးစီးပွားမျှပဋိပက္ခကြေညာ။
ကိုးကား
- 1. Stearn, WT Allium မျိုးစိတ် မည်မျှ သိကြသနည်း။ Kew Mag 1992, 9၊၁၁၃-၁၂၄။ [CrossRef]
- 2. FAOSTAT။ FAO စာရင်းအင်းဒေတာဘေ့စ်။ အွန်လိုင်းတွင် ရနိုင်သည်- http://www.fao.org/2017 (accessed on 8 January 2019).
- 3. ကြက်သွန်ဖြူနှင့် ကြက်သွန်နီ၏ ဓာတုဗေဒကို ပိတ်ဆို့ပါ။ သိပ္ပံ။ နံနက်။ 1985, 252၊၁၁၃-၁၂၄။ [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS ကြွက်တွင်းရှိ antioxidant လုပ်ဆောင်ချက်အပေါ် ကြက်သွန်နီ၏ အကဲဖြတ်ချက်။ Food Chem. Toxicol. 2012, 50, 3912-3919 ။ [CrossRef]
- 5. Lee, S.M.; Moon, J.; Chung, J.H.; Cha, Y.J.; Shin, M.J. Effect of quercetin-rich onion peel extracts on arterial thrombosis in rats. Food Chem. Toxicol. 2013, 57, 99-105 ။ [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. zucker ဆီးချိုရှိသော ကြွက်များတွင် ကြက်သွန်နီ ထုတ်ယူခြင်း၏ အဝလွန်ခြင်း တိုက်ဖျက်ရေး အကျိုးသက်ရောက်မှုများ။ အာဟာရ 2012, 4,1518-1526 ။ [CrossRef]
- 7. Akash, M.S.H.; Rehman, K.; Chen, S. Spice plant Allium cepa: Dietary supplement for treatment of type 2 diabetes mellitus. အစာအာဟာရ 2014, 30၊၁၁၃-၁၂၄။ [CrossRef] [PubMed]
- 8. Wang, Y.; Tian၊ WX; Ma, XF ကြက်သွန်နီ၏ တားမြစ်ဆေးသက်ရောက်မှု ( Allium cepa L.) extract on proliferation of cancer cells and adipocytes via inhibiting fatty acid synthase. Asian Pac. J. Cancer Prev. 2012,13, 5573-5579 ။ [CrossRef] [PubMed]
- 9. လိုင်, WW; ရှုး, SC; Chueh, FS; Chen၊ YY; Yang, JS; လင်း၊ JP; Lien, JC; Tsai, CH; Chung၊ JG Quercetin သည် NF-kappaB နှင့် matrix metalloproteinase-2/-9 အချက်ပြလမ်းကြောင်းများကို ဟန့်တားခြင်းဖြင့် SAS လူ့ခံတွင်းကင်ဆာဆဲလ်များ၏ ရွှေ့ပြောင်းမှုနှင့် ကျူးကျော်ဝင်ရောက်မှုကို ဟန့်တားပေးသည်။ Anticancer Res. 2013, 33၊၁၁၃-၁၂၄။ [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner၊ JA ကြက်သွန်ဖြူ နှင့် ကြက်သွန်နီ - ၎င်းတို့၏ ကင်ဆာကို ကာကွယ်နိုင်သော ဂုဏ်သတ္တိများ။ Cancer Prev. Res. 2015, 8,181-189 ။ [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, အမ်; Rubini, K.; Fini, အမ်; Bigi၊ A. Antioxidant နှင့် quercetin-functionalized hydroxyapatite ၏ အရိုးပြုပြင်ခြင်း ဂုဏ်သတ္တိများ- in vitro osteoblast-osteoclast-endothelial ဆဲလ်တွဲဖက်ယဉ်ကျေးမှုလေ့လာမှု။ Acta Biomater 2016, 32, 298-308 ။ [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; မီကာမီ၊ အမ်; Yagihashi, A. Allium ဟင်းသီးဟင်းရွက် ခုနစ်မျိုးတွင် S-Alk(en)yl-L-cysteine ဆင်းသက်လာမှု ဆယ့်တစ်အရသာ ရှေ့ပြေးနိမိတ်များကို ဖြန့်ဖြူးခြင်း။ Food Sci. Technol. Res. 2011, 17, 55-62 ။ [CrossRef]
- 13. Block, E. Genus Allium ၏ organosulfur ဓာတုဗေဒ—ဆာလဖာ၏ အော်ဂဲနစ်ဓာတုဗေဒအတွက် သက်ရောက်မှုများ။ Angew။ Chem Int အက်ဒ်။ အင်္ဂလိပ် 1992, 31၊၁၁၃-၁၂၄။ [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; သောမတ်စ်, B.; Smith, B. ကြက်သွန်နီ- ကျန်းမာရေးအတွက် ကမ္ဘာလုံးဆိုင်ရာ အကျိုးကျေးဇူးများ။ Phytother. Res. 2002,16, 603-615 ။ [CrossRef]
- 15. Schwimmer, S.; Weston၊ WJ ကြက်သွန်နီတွင် pyruvic အက်ဆစ်၏ Enzymatic ဖွံ့ဖြိုးတိုးတက်မှုသည် pungency တိုင်းတာမှုတစ်ခုဖြစ်သည်။ J. Agric. Food Chem. 1961, 9, 301-304 ။ [CrossRef]
- 16. Ketter, CAT; ကြက်သွန်နီအတွက် Randle၊ WM Pungency အကဲဖြတ်ခြင်း။ ၌ Tested Studies for Laboratory Teaching; Karcher, S.J., Ed.; Association for Biology Laboratory Education (ABLE): New York, NY, USA, 1998; Volume 19, pp. 177-196.
- 17. Hanelt၊ P Taxonomy၊ ဆင့်ကဲဖြစ်စဉ်နှင့် သမိုင်း။ ၌ ကြက်သွန်နီနှင့် မဟာမိတ်သီးနှံများ Vol. I. ရုက္ခဗေဒ၊ ဇီဝကမ္မဗေဒနှင့် မျိုးရိုးဗီဇ၊ Rabinowitch၊ HD၊ Brewster၊ JL၊ Eds။ CRC စာနယ်ဇင်း- Boca Raton, FL, USA, 1990; စစ ၁-၂၆။
- 18. Rabinowitch, HD; Currah, L. Allium သီးနှံသိပ္ပံ- လတ်တလော တိုးတက်မှုများ၊ CABI ထုတ်ဝေခြင်း- Wallingford, UK, 2002။
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Characterization of genetic resources of onion ( Allium cepa L.) from Spanish secondary centre of diversity. ထွာ။ J. Agric Res. 2011, 9၊၁၁၃-၁၂၄။ [CrossRef]
- 20. Ferioli, F.; D'Antuono၊ LF အကဲဖြတ်ခြင်း အီတလီနှင့် ယူကရိန်းတို့မှ ဒေသထွက် ကြက်သွန်နီနှင့် ခရမ်းချဉ်သီးပင်များတွင် phenolics နှင့် cysteine sulfoxides များကို အကဲဖြတ်ခြင်း။ Genet. Resour. Crop Evol. 2016, 63, 601-614 ။ [CrossRef]
- 21. Petropoulos, SA; ဖာနန်ဒက်စ်၊ အေ; Barros, L.; Ferreira, ICFR; Ntatsi၊ G. ဇီဝဗေဒဆိုင်ရာ၊ အာဟာရနှင့် ဓာတုဗေဒဖော်ပြချက်၊ ဂရိနိုင်ငံမှ ကြက်သွန်နီဒေသခံမြေစာပုံ 'vatikiotiko' ၏ ဖော်ပြချက်။ အစားအသောက် Chem ။ 2015,182၊၁၁၃-၁၂၄။ [CrossRef]
- 22. Liguori, L.; Adiletta, G.; နာဇာရို၊ အက်ဖ်; ဖရန်တီယန်နီ၊ အက်ဖ်; Di Matteo, အမ်; မြေထဲပင်လယ်ဒေသရှိ မတူညီသော ကြက်သွန်မျိုးကွဲများ၏ အယ်လ်ဘေးနီးစ်၊ D. ဇီဝဓာတု၊ ဓာတ်တိုးဆန့်ကျင်ဂုဏ်သတ္တိများနှင့် ပိုးသတ်နိုင်သော လုပ်ဆောင်ချက်။ J. Food Meas စာရိတ္တ။ 2019,13၊၁၁၃-၁၂၄။ [CrossRef]
- 23. Yoo, KS; Pike, L.; Crosby, K.; Jones, R.; Leskovar, D. မျိုးစေ့များ၊ ကြီးထွားမှုပတ်ဝန်းကျင်နှင့် မီးသီးအရွယ်အစားများကြောင့် ကြက်သွန်နီအဆိပ်သင့်ခြင်း ကွာခြားချက်များ။ သိပ္ပံပညာ။ Hortic 2006,110၊၁၁၃-၁၂၄။ [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; ဂျော့ခ်ျအီး; Kroh, LW; Rohn၊ S. မျိုးရိုးအမျိုးအစားအလိုက် လွှမ်းမိုးထားသော ကြက်သွန်နီမီးသီး၏ မတူညီသော အစိတ်အပိုင်းများတွင် quercetin-3၊ 4′-O-diglucoside၊ quercetin-4′-O-monoglucoside နှင့် quercetin ဖြန့်ဖြူးခြင်း။ အစားအသောက် Chem ။ 2010,122, 566-571 ။ [CrossRef]
- 25. Caruso, G.; Conti, S.; ဗီလာရီ၊ G.; Borrelli, C.; Melchionna, G.; Minutolo, အမ်; Russo, G.; Amalfitano, C. ကြက်သွန်နီ၏ အထွက်နှုန်း၊ အရည်အသွေးနှင့် ဓာတ်တိုးဆန့်ကျင်ပစ္စည်း ပါဝင်မှုအပေါ် စိုက်ချိန်နှင့် အပင်သိပ်သည်းဆ၏ အကျိုးသက်ရောက်မှုများ ( Allium cepa L.) အီတလီတောင်ပိုင်း။ သိပ္ပံပညာ။ Hortic 2014,166၊၁၁၃-၁၂၄။ [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, ဂျေ; Simal-Gandara, J.; Rodrigues, AS; Almeida၊ DPF သည် antioxidant flavonoids အရင်းအမြစ်အဖြစ် ကြက်သွန်နီ၏ ထပ်လောင်းတန်ဖိုးကို တိုးမြှင့်ခြင်း- အရေးကြီးသော သုံးသပ်ချက်။ Crit ။ ဗျာစားနပ်ရိက္ခာသိပ္ပံ။ Nutr ။ 2014, 54,1050-1062 ။ [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweigert, RM; Carle, R. ကြက်သွန်နီတွင် ပျော်ဝင်နိုင်သော ကာဗိုဟိုက်ဒရိတ်နှင့် အညှောင့်အခြေခံမူများအပေါ် စိုက်ပျိုးနည်းနှင့် စိုက်ပျိုးရွေးချယ်မှုအပေါ် သက်ရောက်မှု ( Allium cepa L.) J. Agric. Food Chem. 2018, 66၊၁၁၃-၁၂၄။ [CrossRef] [PubMed]
- 28. Tedesco, I.; Carbone, V.; Spagnuolo, C.; Minasi, P.; Russo, G.L. Identification and quantification of flavonoids from two southern Italian cultivars of allium cepa L., Tropea (red onion) and Montoro (copper onion), and their capacity to protect human erythrocytes from oxidative stress. J. Agric. Food Chem. 2015, 63, 5229-5238 ။ [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. ကြက်သွန်နီတွင် ဖြတ်တောက်နိုင်သော မျိုးဗီဇရိုက်ထည့်ခြင်းသည် မျိုးရိုးဗီဇကွဲပြားမှုနှင့် မော်လီကျူးမွေးမြူမှုအတွက် အသုံးဝင်သော သတင်းအချက်အလက်ဆိုင်ရာ SNPs များဖွဲ့စည်းပုံကို ဖော်ပြသည်။ မောလ် ဖောက်။ 2019, 39, 5 ။ [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri၊ F အီတလီ တာရှည်ခံ ခရမ်းချဉ်သီး၏ မျိုးရိုးဗီဇ ကွဲလွဲမှု (Solanum lycopersicum L.) SSR နှင့် morphological fruit traits များကို အသုံးပြု၍ စုဆောင်းခြင်း။ Genet. Resour. Crop Evol. 2014, 62, 721-732 ။ [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar၊ C. ကြက်သွန်အစုအဝေးတွင် မျိုးရိုးဗီဇ ကွဲပြားမှုနှင့် အရည်အသွေး စရိုက်လက္ခဏာများကို ရှာဖွေခြင်း။ ( Allium cepa L.) စပိန်အနောက်မြောက်ပိုင်းမှ တောင်တန်းများ။ မျိုးရိုးဗီဇ 2015, 47, 885-900 ။ [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo၊ C.; Pavan, S.; Ricciardi၊ L. မျိုးရိုးဗီဇ၊ ကိုက်လန်၏ ဇီဝစိုက်ပျိုးရေးဆိုင်ရာနှင့် အာဟာရဆိုင်ရာလက္ခဏာရပ်များ (Brassica oleracea ဖြစ်သည် L. var. acephala) အီတလီတောင်ပိုင်း၊ Apulia ရှိ ကွဲပြားမှု။ မတူကွဲပြားခြင်း 2018,10, 25 ။ [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. မျိုးရိုးဗီဇခွဲခြမ်းစိတ်ဖြာရန်ခုခံ Orobanche crenata (ခက်ရင်း။) ပဲစေ့ (Pisum sativum L.) low-strigolactone လိုင်း။ J. Plant Pathol. 2016, 98, 671-675 ။
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo၊ M. ကြက်သွန်နီကို စည်းထားသောအချိန်ကို bolting ပြုလုပ်ရန်အတွက် quantitative trait loci ကို ပုံဖော်ခြင်း ( Allium fistulosum L.) ယူဖီတီကာ 2016, 209, 537-546 ။ [CrossRef]
- 35. Dhaka, N.; Mukhopadhay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan၊ AK သည် မျိုးရိုးဗီဇ SSR များကို ဖော်ထုတ်ခြင်းနှင့် SSR အခြေပြု ချိတ်ဆက်မှုမြေပုံတစ်ခု တည်ဆောက်ခြင်း Brassica juncea။ ယူဖီတီကာ 2017, 213, 15 ။ [CrossRef]
- 36. Anandhan, S.; Mote, S.R.; Gopal, J. Evaluation of onion varietal identity using SSR markers. မျိုးစေ့သိပ္ပံ။ နည်းပညာ။ 2014, 42, 279-285 ။ [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. ချက်သမ္မတနိုင်ငံမှ ကြက်သွန်နီမျိုးစိတ်များ ကွဲပြားမှုအတွက် သတ်မှတ်အမှတ်အသားတစ်ခု၏ ရွေးချယ်မှုနှင့် တရားဝင်မှု။ Czech J. Genet အပင်မျိုးစေ့။ 2015, 51, 62-67 ။ [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. Apulian သံလွင်ပိုးမွှား ဇီဝမျိုးစုံမျိုးကွဲများ၏ ထိန်းသိမ်းခြင်းနှင့် လက္ခဏာရပ်များ။ Acta Hortic 2018,1199,1-6 ။ [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. Assessing the genetic diversity of Spanish allium cepa မိုက်ခရိုဂြိုလ်တု အမှတ်အသားများကို အသုံးပြု၍ ကြက်သွန်မွေးမြူရန်အတွက် မြေနေရာများ။ သိပ္ပံပညာ။ Hortic 2014,170၊၁၁၃-၁၂၄။ [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Ulloa, A.; Pomar, F.; Silvar, C. Assessing the genetic diversity in onion (allium cepa L.) စပိန်အနောက်မြောက်ပိုင်းမှ ကုန်းမြေများနှင့် ဥရောပကွဲပြားမှုများနှင့် နှိုင်းယှဉ်ခြင်း။ N. Z. J. Crop Hortic. 2016, 44၊၁၁၃-၁၂၄။ [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; မန်ဂီနီ၊ G.; Montemurro, C.; Ricciardi, L.; Lotti, C. ကုလားပဲ၏ ကမ္ဘာလုံးဆိုင်ရာ ပိုးမွှားအစုအဝေး၏ မျိုးရိုးဗီဇကွဲလွဲမှု (Cicer arietinum L.) မျိုးရိုးဗီဇတိုက်စားမှုအန္တရာယ်ရှိ အီတလီအသုံးပြုမှုများ အပါအဝင်။ Physiol။ မောလ် Biol အပင်များ 2017, 23၊၁၁၃-၁၂၄။ [CrossRef]
- 42. Mazzeo, R.; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti၊ C. ဘရိုကိုလီ ခွေးရူးပြန်ရောဂါတွင် မျိုးရိုးဗီဇ ကွဲပြားမှု (Brassica rapa L. subsp. sylvestri (L.) Janch.) အီတလီတောင်ပိုင်း။ သိပ္ပံပညာ။ Hortic 2019, 253၊၁၁၃-၁၂၄။ [CrossRef]
- 43. Jakse, M.; မာတင်၊ ဒဗလျူ; McCallum, J.; Havey၊ M. Single nucleotide polymorphisms၊ indels နှင့် ရိုးရှင်းသော sequence သည် ကြက်သွန်မျိုးစိတ်အမျိုးအစားခွဲခြားခြင်းအတွက် ထပ်တလဲလဲလုပ်သည်။ J. Am Soc Hortic သိပ္ပံပညာ။ 2005,130, 912-917 ။ [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel၊ F. မျိုးရိုးဗီဇ ကွဲပြားမှု ခွဲခြမ်းစိတ်ဖြာမှုနှင့် single-nucleotide polymorphism အမှတ်အသားများ ဖော်ပြထားသော အစီအစဥ် တဂ်-ရိုးရှင်းသော အစီအစဥ် ထပ်ခါထပ်ခါ အမှတ်အသားများကို အခြေခံ၍ စိုက်ပျိုးထားသော မီးသီးကြက်သွန်နီ ဖွံ့ဖြိုးတိုးတက်မှု။ J. Am Soc Hortic သိပ္ပံပညာ။ 2008,133, 810-818 ။ [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; ရိုက် K.; Chen, L.; McCallum၊ J. သည် ကြက်သွန်နီအတွင်းနှင့် မီးသီးအတွင်း မျိုးဗီဇကွဲပြားမှုကို ခန့်မှန်းရန်အတွက် ခိုင်မာသော မျိုးရိုးဗီဇရိုးရှင်းသော ဆင့်ကဲဖြစ်စဉ်ကို ထပ်ခါထပ်ခါ အမှတ်အသားပြုခြင်း ( Allium cepa L.) populations. မောလ် ဖောက်။ 2012, 30၊၁၁၃-၁၂၄။ [CrossRef]
- 46. DeWoody, J.A.; Honeycutt, R.L.; Skow, L.C. Microsatellite markers in white tailed deer. J. Hered 1995, 86, 317-319 ။ [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. အီရန်ကြက်သွန် ( Allium cepa L.) cultivars responses to inbreeding depression. ကမ္ဘာ့အက်ပလီကေးရှင်း သိပ္ပံပညာ။ ည။ 2010,11, 426-428 ။
- 48. Abdou, R.; Bakasso, Y.; Saadou, အမ်; Baudoin, JP; Hardy၊ OJ နိုင်ဂျာကြက်သွန်နီ၏မျိုးရိုးဗီဇကွဲပြားမှု ( Allium cepa L.) ရိုးရိုး sequence repeat markers (SSR) ဖြင့် အကဲဖြတ်သည်။ Acta Hortic 2016,1143, 77-90 ။ [CrossRef]
- 49. Pavan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al ။ ဂျီနိုမ်ကျယ်ပြန့်သော အမှတ်အသားရှာဖွေတွေ့ရှိမှုနှင့် မျိုးဗီဇရိုက်ခြင်းတို့ဖြင့် ဖော်ပြထားသည့်အတိုင်း စိုက်ပျိုးထားသော ကုလားပဲတွင် ထင်ရှားသော မျိုးရိုးဗီဇအစုအဝေးတစ်ခု။ Plant Genome 2017, 2017,10 ။ [CrossRef]
- 50. Pavan, S.; Marcotrigiano, A.R.; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotyping-by-sequencing of a melon (Cucumis melo L.) မတူကွဲပြားမှု၏အလယ်တန်းဗဟိုမှ ပိုးမွှားစုဆောင်းမှုသည် မျိုးရိုးဗီဇကွဲလွဲမှုပုံစံများနှင့် မတူညီသောမျိုးရိုးဗီဇပေါင်းကူးကန်များ၏ genomic features များကို မီးမောင်းထိုးပြသည်။ BMC Genom. 2017, 18, 59 ။ [CrossRef]
- 51. Di Rienzo, V.; Sion, S.; Taranto, F.; D’Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. Genetic flow among olive population within the Mediterranean basin. ရွယ်တူ ဂျေ 2018, 6. [CrossRef]
- 52. Shepherd, LD; McLay၊ TG သည် polysaccharide ကြွယ်ဝသော အပင်တစ်သျှူးမှ DNA ကို သီးခြားခွဲထုတ်ရန်အတွက် micro-scale protocol နှစ်ခု။ J. Plant Res. 2011,124, 311-314 ။ [CrossRef]
- 53. Doyle, J.J.; Doyle, J.L. Isolation of plant DNA from fresh tissue. focus 1990,12၊၁၁၃-၁၂၄။
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; မာတင်၊ ဒဗလျူ; Zewdie, Y.; McCallum, J.; Catanach, A.; ရပ်သာဖို့ဒ်၊ P.; နစ်၊ KC; Jenderek, အမ်; et al ။ ကြက်သွန်နီ 11,008 လုံး၏ ထူးခြားသောအစုတစ်ခုသည် ဖော်စပ်ထားသော အစီအစဥ်နှင့် မိုနိုကော့တ်အမှာစာ asparagales နှင့် poales များကြားတွင် ဖော်ပြထားသော အစီအစဥ်နှင့် မျိုးဗီဇကွဲပြားမှုများကို ဖော်ပြသည်။ အပင်ဆဲလ် 2004,16, 114-125 ။ [CrossRef]
- 55. Kim, HJ; Lee, HR; ဟွန်း၊ JY; သီချင်း၊ KH; Kim, KH; Kim, JE; Hur၊ CG; SSR Finder ကို အသုံးပြု၍ ကြက်သွန်မျိုးဗီဇ သန့်စင်မှု စမ်းသပ်ခြင်းအတွက် Harn၊ CH Marker ဖွံ့ဖြိုးတိုးတက်မှု။ Korean J. Breed. သိပ္ပံပညာ။ 2012, 44, 421-432 ။ [CrossRef]
- 56. Schuelke, M. An economic method for fluorescent labeling of PCR fragments. နတ် ဇီဝနည်းပညာ။ 2000, 18, 233-234 ။ [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse၊ PE GenAlEx 6.5- Excel ရှိ မျိုးရိုးဗီဇခွဲခြမ်းစိတ်ဖြာခြင်း။ သင်ကြားရေးနှင့် သုတေသနအတွက် လူဦးရေမျိုးရိုးဗီဇဆော့ဖ်ဝဲ- အပ်ဒိတ်တစ်ခု။ ကွန်ပြူတာအသုံးချဇီဝဗေဒ 2012, 28, 2537-2539 ။ [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC ကွန်ပြူတာပရိုဂရမ် CERVUS သည် genotyping error ကို လိုက်လျောညီထွေဖြစ်အောင် မည်သို့ပြန်လည်သုံးသပ်ခြင်းသည် ဖခင်တာဝန်ကို အောင်မြင်စေပါသည်။ မောလ် Ecol 2007,16၊၁၁၃-၁၂၄။ [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Association သည် ဖွဲ့စည်းတည်ဆောက်ထားသော လူဦးရေအတွက် မြေပုံဆွဲခြင်း။ Am. J. Hum. Genet. 2000, 67, 170-181 ။ [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. ဆော့ဖ်ဝဲလ်ဖွဲ့စည်းပုံအား အသုံးပြု၍ လူတစ်ဦးချင်းစီ၏အစုအဝေးအရေအတွက်ကို ထောက်လှမ်းခြင်း- သရုပ်ပြလေ့လာမှု။ မောလ် Ecol 2005,14, 2611-2620 ။ [CrossRef]
- 61. Earl, D.; VonHoldt၊ B. STRUCTURE HARVESTER- STRUCTURE output ကိုမြင်ယောင်ပြီး Evanno နည်းလမ်းကိုအကောင်အထည်ဖော်ရန်အတွက် ဝဘ်ဆိုက်နှင့်ပရိုဂရမ်။ Conserv. Genet. Resour. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW- allele ကြိမ်နှုန်းဒေတာမှ လူဦးရေသစ်ပင်များတည်ဆောက်ခြင်းနှင့် အခြားပမာဏအချို့ကိုတွက်ချက်ခြင်းအတွက် POPTREE ဝက်ဘ်ဗားရှင်း။ မောလ် Biol ဆင့်ကဲ။ 2014, 31, 1622-1624 ။ [CrossRef]
- 63. Kumar, S.; Stecher, G.; လီ၊ အမ်; Knyaz, C.; Tamura, K. MEGA X. Molecular Evolutionary Genetics Analysis သည် ကွန်ပျူတာပလက်ဖောင်းများတစ်လျှောက်။ မောလ် Biol ဆင့်ကဲ။ 2018, 35၊၁၁၃-၁၂၄။ [CrossRef]